Nat Methods:利用ATAC-see技术可视化观察易接近的染色质
2017-01-09 佚名 生物谷
在有限的细胞核空间中,基因组的大部分是紧密折叠的,仅留下需要转录的部分是易接近的。美国斯坦福大学的Howard Chang说,人们有“巨大的兴趣”来确定一个给定的细胞类型中哪些基因组区域是有活性的。这正是Chang开发一种被称作ATAC-seq(Assay for Transposase-Accessible Chromatin with highthroughput sequencing, 利
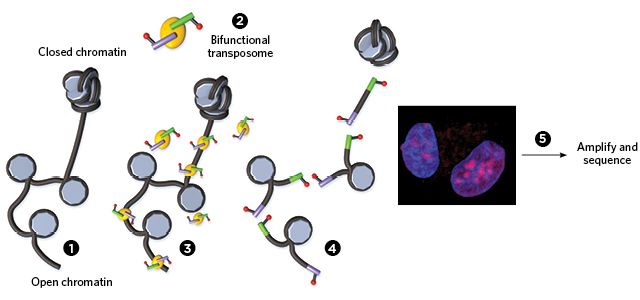
Chang在2013年就描述了ATAC-seq,但是他说,“我们是让细胞破碎来获得这种信息,因此我们不能了解这些易接近的基因组区域的三维结构。”
三年过去了。Chang如今开发出ATAC-see(assay of transposase-accessible chromatin with visualization, 利用可视化检测转座酶易接近的染色质)技术。这种技术利用与ATAC-seq相同的酶学方法来整合DNA标记,不同的是,与这些DNA标记相偶联的荧光团允许他们可视化观察到三维的固定不动的细胞核。而且,一旦观察到这些细胞,通过测序就能够鉴定出发生标记的区域。
利用ATAC-see技术,Chang团队发现不同于大多数细胞的是,在中性粒细胞内,易接近的染色质倾向于位于细胞核的边缘。这种分布似乎促进中性粒细胞胞外陷阱(neutrophil extracellular trap, NET)形成。NET是中性粒细胞重要的杀菌利器。这种细胞直接把自己的DNA和组蛋白吐到胞外,形成一个网状的陷阱来捕捉和杀死病原菌。然而,NET也能够促进癌症转移。
Chang团队也利用ATAC-see技术来研究在细胞周期期间,整个基因组的易接近性如何发生变化。
美国马萨诸塞大学医学院的Job Dekker(未参与这项研究)说,“染色质研究领域的重大挑战之一就是将利用基因组方法获得的数据与利用成像法获得的数据整合在一起。因此,针对这种检测技术,我喜欢的一点就是它将这两者结合在一起。”
|
易接近的染色质检测技术 |
检测原理 |
技术难易性 |
能否可视化 |
用于测序所需的细胞数量 |
|
DNase-seq |
脱氧核糖核酸酶I(DNase I)偏好性地消化易接近的DNA。核苷酸接头连接到这些已被消化的DNA链上,然后利用这些接头对这些已被消化的区域进行分离和测序。 |
比较困难,特别需要优化消化条件 |
不能 |
上百万个 |
|
ATAC-see |
转座酶将荧光标记的DNA测序接头(标记)插入到易接近的染色质中,然后利用这些标记对DNA进行可视化观察、扩增和测序。 |
对那些熟悉标准的分子技术的人而言,相对比较简单 |
能 |
5万个。ATAC-seq(缺乏荧光可视化观察到的检测技术)已在单个细胞中检测过,因此这可能是可行的。
|
原始出处
Xingqi Chen, Ying Shen, Will Draper, Jason D Buenrostro, Ulrike Litzenburger.et.al.ATAC-see reveals the accessible genome by transposase-mediated imaging and sequencing.Nat Methods.2016
本网站所有内容来源注明为“梅斯医学”或“MedSci原创”的文字、图片和音视频资料,版权均属于梅斯医学所有。非经授权,任何媒体、网站或个人不得转载,授权转载时须注明来源为“梅斯医学”。其它来源的文章系转载文章,或“梅斯号”自媒体发布的文章,仅系出于传递更多信息之目的,本站仅负责审核内容合规,其内容不代表本站立场,本站不负责内容的准确性和版权。如果存在侵权、或不希望被转载的媒体或个人可与我们联系,我们将立即进行删除处理。
在此留言







#MET#
22
#可视化#
31
#TAC#
32
#Nat#
30
#ATA#
24
#染色质#
26